 返回新闻动态
返回新闻动态
苏州必扬医药科技有限公司参加了 OpenADMET 与 Expansion Therapeutics 联合举办的 ADMET 盲测挑战赛(OpenADMET - ExpansionRx Blind Challenge,2025.10.27–2026.01.19)。

OpenADMET是一个开放的公共科学倡议,旨在通过构建高质量数据集、开发计算模型及举办盲测挑战赛,推动小分子药物ADMET(吸收、分布、代谢、排泄和毒性)性质预测领域的发展。该项目由多机构协作推进,目前已获得ARPA-H、盖茨基金会等资助,并由开放分子软件基金会(OMSF)负责运营管理。Expansion Therapeutics 是一家专注于 RNA 介导疾病(如强直性肌营养不良、ALS)药物研发的生物技术公司,此次将其临床前优化项目中系统采集的 7,000 余个分子的高质量 ADME 数据开源共享,该数据集构成目前可公开获取的、规模最大的模拟先导化合物优化过程的数据集之一。使用时间切分的评估方式,即基于历史上已有的化合物进行训练并预测后续设计分子的性质,高度贴近工业界的先导化合物优化流程。该流程中,过去的实验数据指导着未来的分子设计决策,这为评估模型的前瞻性预测能力提供了一个稀缺的工业级基准。
本次挑战赛聚焦于9项ADME(吸收、分布、代谢、排泄)领域的经典性质预测,包括:LogD、动力学溶解度、小鼠/人肝微粒体清除率、Caco-2外排比、Caco-2表观渗透系数A>B、小鼠血浆蛋白结合率(MPPB)、小鼠脑组织蛋白结合率(MBPB)以及小鼠腓肠肌结合率(MGMB)。
本次竞赛吸引了来自工业界与学术界的370多位参与者,背景与经验水平各异。在前十名提交方案中,已确认多家领先机构:默克(Merck)位列第3(提交名称:moka)、Deepmirror位列第4(提交名称:campfire capillary)。部分前十名参与者的所属机构尚未公开。
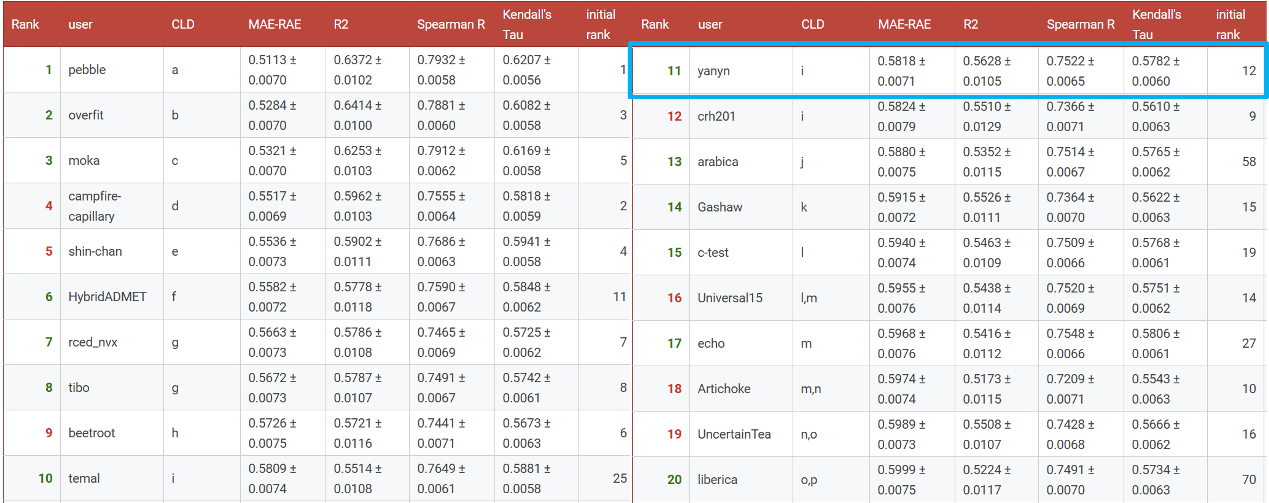
图1. OpenADMET - ExpansionRx 盲测挑战赛最终排行榜。
苏州必扬医药科技有限公司(提交名称:yanyn)在本次竞赛中获得第11名(图1),在这一高度贴近工业实践的评估中,我们的方法展现出与国际前沿方案可比的泛化能力(图2)。需要指出的是,我们的模型仅基于挑战赛官方提供的训练集(LogD除外)进行训练,未引入外部或内部补充数据,在纯粹的数据约束条件下仍取得了具备工业参考价值的预测性能,体现了方法本身的稳健性与实用潜力。展望未来,在进一步优化方法学的基础上,我们计划整合公开及内部数据集,以探索模型性能的进一步提升空间。
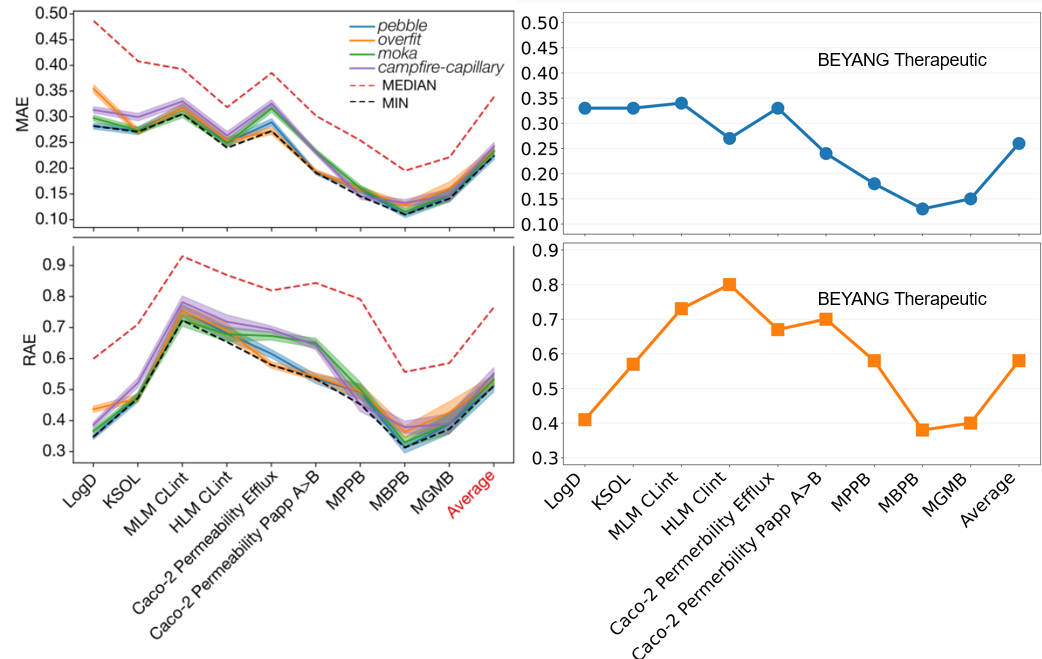
图2,左图展示了 OpenADMET 官网公布的挑战赛综合分析结果,汇总了排名前四团队及全部参赛方案的性能分布;右图为我们团队的提交结果。
方法学概述
采用 Chemprop 模型 [1],该模型基于消息传递神经网络(Message Passing Neural Network, MPNN),是图神经网络(GNN)中广泛应用的方法。在排名前20的参赛队伍中,有18支使用了该算法。
采用 CheMeleon 预训练模型 [2],该模型基于 Mordred 工具包生成的确定性分子描述符进行预训练。
采用 Kinetic GROVER 多任务模型(KERMT)[3],这是一种面向分子性质预测的预训练图神经网络模型。该方法在论文研究中接受了测试,并在多任务预测场景中展现出了良好效果 [4]。
任务配置
训练集:除 logD 任务使用了外部数据外,其余所有任务均仅依赖竞赛官方提供的数据集进行训练。
验证策略:在训练集上采用分层10折交叉验证(stratified 10-fold cross-validation),以确保性能评估的统计稳健性。
超参数设置:Chemprop 与 CheMeleon 基础模型均使用多组不同的超参数配置进行训练与评估;KERMT 模型则采用了两种预训练模型主干架构——GROVERbase, GROVERlarge [5]。
学习范式:
除 logD 外,所有任务均在多任务学习(multi-task learning)框架下进行训练;
logD 任务利用公开可用数据,以单任务模型形式进行训练,数据预处理采用了 Adrian 等人提出的去噪方法 [6]。
分子描述符类型:针对 CheMeleon 与 Chemprop 模型,共评估了四种分子表示方案:
内置默认表示(default)
RDKit 描述符(rdkit)
Morgan 二值指纹(morgan_binary)
Morgan 计数型指纹(morgan_count)
模型选择与集成策略
交叉验证排名:此方法用于参数选择。在多任务预测中,若某个参数配置在至少3个(共9个)任务中,其交叉验证平均绝对误差(MAE)均位列单个任务前10%,则该配置将被保留。
外部验证筛选:上一步选择好的模型在主办方提供的独立验证集上进行外部验证。
任务特定阈值筛选:在集成构建前,针对每个任务分别设定性能阈值(task-specific cutoff)。仅保留满足该任务阈值要求的模型参与后续集成。
任务级直接集成:对于每个任务,所有通过阈值筛选的模型直接进行集成,生成该任务的最终预测结果。不同任务采用独立的集成模型,而非共享统一集成器。
结果提交:各任务的集成预测结果作为官方最终提交结果。
参考文献
1. Chemprop v2: An Efficient, Modular Machine Learning Package for Chemical Property Prediction. Graff DE, Morgan NK, Burns JW, Doner AC, Li B, Li SC, Manu J, Menon A, Pang HW, Wu H, Zalte AS, Zheng JW, Coley CW, Green WH, Greenman KP. J Chem Inf Model. 2026 Jan 12;66(1):28-33. doi: 10.1021/acs.jcim.5c02332. Epub 2025 Dec 26. PMID: 41453060.
2. Descriptor-based Foundation Models for Molecular Property Prediction. Jackson Burns, Akshat Zalte, William Green. https://doi.org/10.48550/arXiv.2506.15792
3. Multitask finetuning and acceleration of chemical pretrained models for small molecule drug property prediction. Matthew Adrian, Yunsie Chung, Kevin Boyd, Saee Paliwal, Srimukh Prasad Veccham, Alan C. Cheng
https://doi.org/10.48550/arXiv.2510.12719
4. Multitask finetuning and acceleration of chemical pretrained models for small molecule drug property prediction. Matthew Adrian, Yunsie Chung, Kevin Boyd, Saee Paliwal, Srimukh Prasad Veccham, Alan C. Cheng.
https://doi.org/10.48550/arXiv.2510.12719
5. Self-Supervised Graph Transformer on Large-Scale Molecular Data. Yu Rong, Yatao Bian, Tingyang Xu, Weiyang Xie, Ying Wei, Wenbing Huang, Junzhou Huang. https://doi.org/10.48550/arXiv.2007.02835
6. Denoising Drug Discovery Data for Improved Absorption, Distribution,Metabolism, Excretion, and Toxicity Property Prediction. Matthew Adrian, Yunsie Chung, and Alan C. Cheng. Journal of Chemical Information and Modeling 2024 64 (16), 6324-6337. DOI: 10.1021/acs.jcim.4c00639




